# GEO
**Repository Path**: ZXY529/GEO
## Basic Information
- **Project Name**: GEO
- **Description**: No description available
- **Primary Language**: Unknown
- **License**: Not specified
- **Default Branch**: master
- **Homepage**: None
- **GVP Project**: No
## Statistics
- **Stars**: 0
- **Forks**: 0
- **Created**: 2019-09-21
- **Last Updated**: 2020-12-19
## Categories & Tags
**Categories**: Uncategorized
**Tags**: None
## README
# 表达矩阵分析大全
Note : Please **don't use it** if you are not the fan of our [biotrainee](http://www.bio-info-trainee.com/), Thanks.
### 来龙去脉
GEO数据库挖掘系列知识分享课程,于2016年首发于生信菜鸟团博客:http://www.bio-info-trainee.com/2087.html
配套教学视频在B站:https://www.bilibili.com/video/av26731585/
早期目录如下:
- 第一讲:GEO,表达芯片与R
- 第二讲:从GEO下载数据得到表达量矩阵
- 第三讲:对表达量矩阵用GSEA软件做分析
- 第四讲:根据分组信息做差异分析
- 第五讲:对差异基因结果做GO/KEGG超几何分布检验富集分析
- 第六讲:指定基因分组boxplot指定基因list画热图
- 第七讲:根据差异基因list获取string数据库的PPI网络数据
- 第八讲:PPI网络数据用R或者cytoscape画网络图
- 第九讲:网络图的子网络获取
- 第十讲:hug genes如何找
### 2018年更新版
2018是一个特殊的年份,我们生信技能树落地了很多线下分享会,作为创始人我身先士卒准备了非常多的干货教程,在B站免费分享 74小时的生物信息学系列视频课程:
1.[3个学生的linux视频学习笔记](http://mp.weixin.qq.com/s?__biz=MzAxMDkxODM1Ng==&mid=2247488597&idx=1&sn=14592219254572110934185881c3b92e&chksm=9b4854eeac3fddf838ca9a249a5b263719a802dda45f7fc29828bf4d96a91057bc2658381a6f&scene=21#wechat_redirect)
2.[生信人应该这样学R语言系列视频学习心得笔记分享](http://mp.weixin.qq.com/s?__biz=MzAxMDkxODM1Ng==&mid=2247488613&idx=1&sn=90385ff03cc78bcc44484d32cf2068c6&chksm=9b4854deac3fddc82b6fadd1a17975cd682b6fadc37d3288b12c955b5515d5345e1aa6e40b43&scene=21#wechat_redirect)
3.[一万人陪你学习GEO数据库挖掘知识(公益视频听课笔4.记分享)](http://mp.weixin.qq.com/s?__biz=MzAxMDkxODM1Ng==&mid=2247488674&idx=1&sn=591ff48ff2bf7a5fafc79b8d8a876cd3&chksm=9b485419ac3fdd0f27e54bcc3be4dc56e9c4c1890f1508d582ee22870faa7e18d53be2d26171&scene=21#wechat_redirect)
5.[公共数据库挖掘视频学习心得体会](http://mp.weixin.qq.com/s?__biz=MzAxMDkxODM1Ng==&mid=2247488675&idx=1&sn=91263a01b5bc78cedf330471ccef7efa&chksm=9b485418ac3fdd0e9df13f4506ba7b790ba3473fbc66d1418d2ed76d768efec082b2e4147a95&scene=21#wechat_redirect)
6.[生信小技巧系列第一季完结版视频教程学习笔记分享](http://mp.weixin.qq.com/s?__biz=MzAxMDkxODM1Ng==&mid=2247488752&idx=1&sn=a3b0aae5ee927b69c1be2f66363c57ea&chksm=9b48544bac3fdd5d1b7a7f6265f4e66006fa8a87020ac52c4c0693dedb556f1ddfbb657e95ef&scene=21#wechat_redirect)
本项目主要是GEO数据库挖掘课程的代码仓库,记住,下面的每个文件夹都值得你拿出**50个小时以上的时间**来学习。
### 仓库概括
主要项目代码文件夹:
- GSE42872_main,主要演示GEO数据库挖掘的标准6步骤
- GSE11121_surivival,主要演示基于基因表达量分组的批量生存分析
六个任务项目文件夹:
- task1-check-specific-genes , 主要演示检查自己感兴趣的基因在多个GSE数据集表现情况
- task2-lncRNA-mRNA-network , 主要演示如何构建网络
- task3-multiple-groups , 主要演示,如果样本分组信息非常复杂该如何进行下游分析
- task4-NPC, 主要演示GEO数据库挖掘的标准6步骤,跟GSE42872_main类似
- task5-dynamic-network-biomarker,主要演示新的算法,超脱于GSE42872_main展示的GEO数据库挖掘的标准6步骤
- task6-GEO-TCGA,主要演示如何结合TCGA数据库
两个额外补充项目文件夹:
- airway_RNAseq,主要演示如果是RNA-seq得到的表达矩阵该如何分析,与传统芯片表达矩阵的异同
- breast_cancer_meta-analysis , 主要演示如何进行meta分析。
下面是主要代码文件夹 `GSE42872_main` 代码的展示:
### Then run step1 : download data
数据是灵魂!
It always not very easy to download data if you are in China, so I also upload the file `GSE42872_raw_exprSet.Rdata` , you can load it directly.
```r
if(F){
library(GEOquery)
gset <- getGEO('GSE42872', destdir=".",
AnnotGPL = F,
getGPL = F)
save(gset,'GSE42872.gset.Rdata')
}
load('GSE42872_eSet.Rdata')
b = eSet[[1]] # 看清楚,某些GSE数据集有多个平台,注意挑选
raw_exprSet=exprs(b)
group_list=c(rep('control',3),rep('case',3))
save(raw_exprSet,group_list,
file='GSE42872_raw_exprSet.Rdata')
```
### Then step2: check the expression matrix
高质量的数据是保障!
Try to understand my codes, how did I filter the probes by the annotation of each microarry, and how I check the group information for the different samples in each experiment.
Including PCA and Cluster figures, as below:
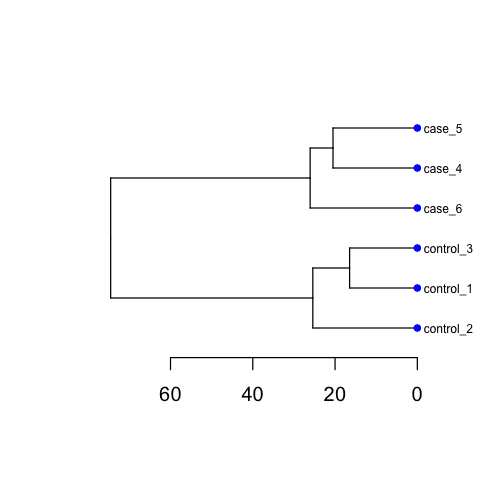
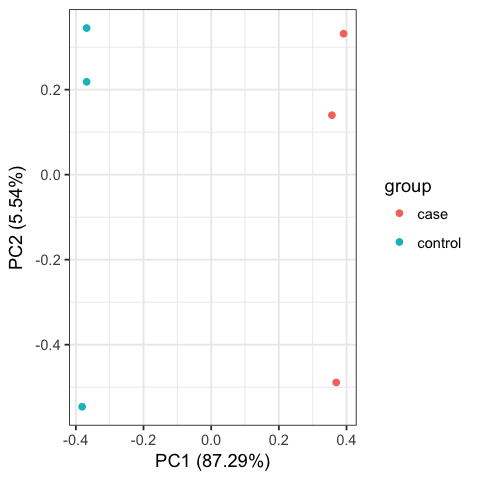
Please ensure that you do run those codes by yourself !!!
### Then step3: do DEG analysis
差异分析是核心流程
Normally we will do differential expression analysis for the microarray, and LIMMA is one of the best method, so I just use it. If the expression matrix(raw counts ) comes from mRNA-seq, you can also choose DESeq based on negative binomial (NB) distributions or baySeq and EBSeq.
Once DEG finished, we can choose top N genes for heatmap as below:
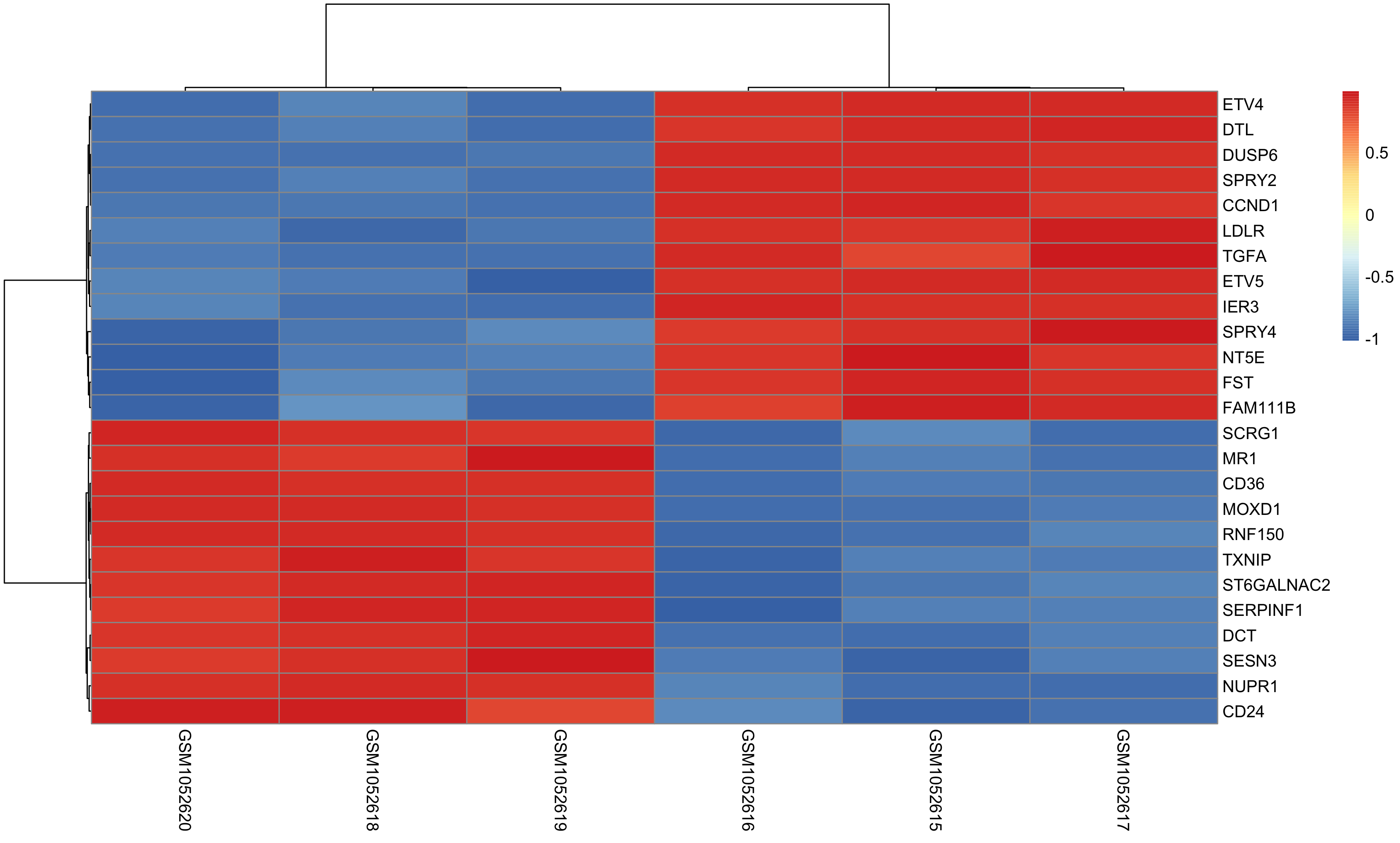
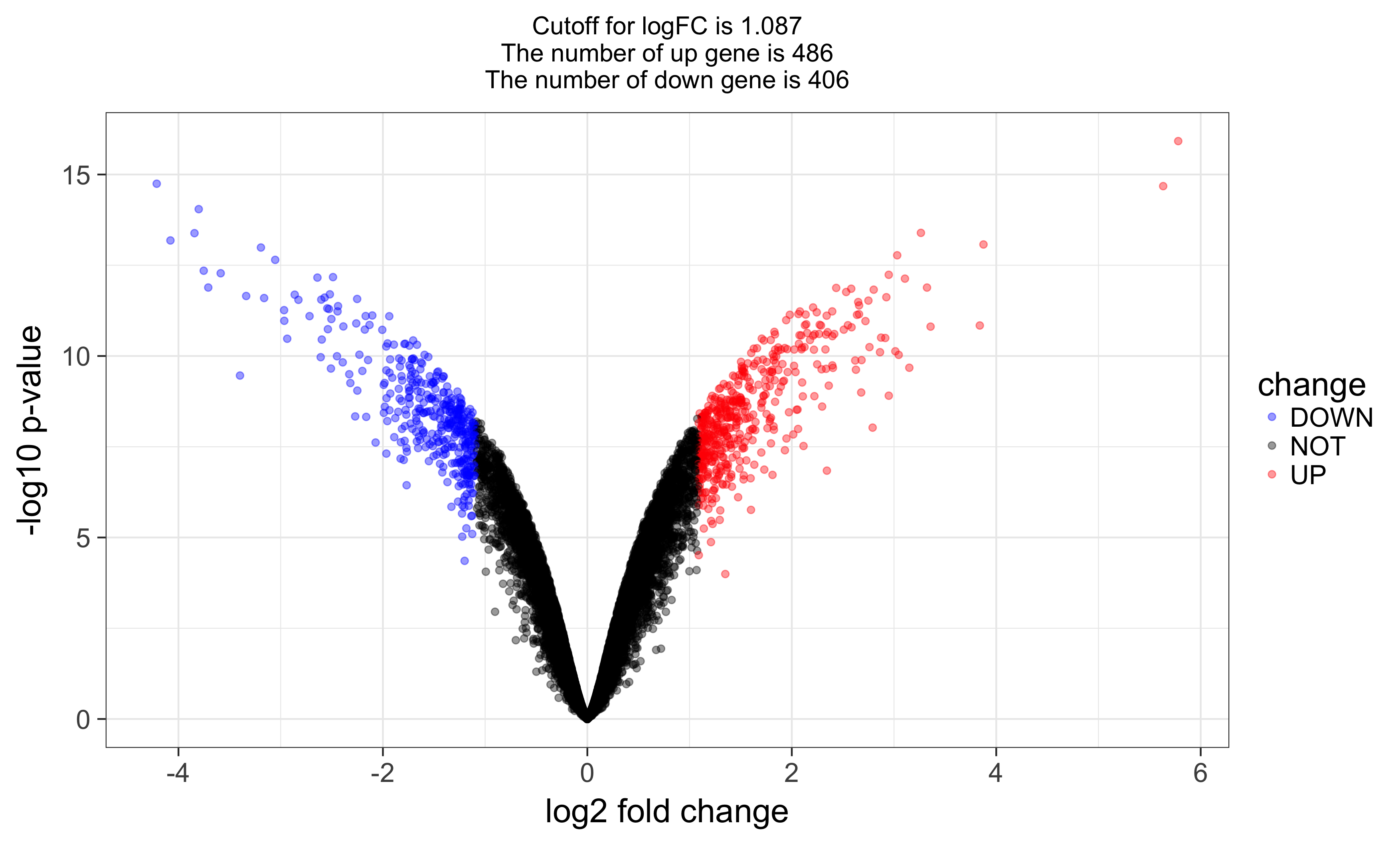
and volcano plot as below:
### Then step4 : annotation for GO and KEGG database
数据库的注释是升华!
Annotation for the significantly changed genes, over-representation test or GSEA for GO/KEGG/biocarta/rectome/MsigDB and so on.
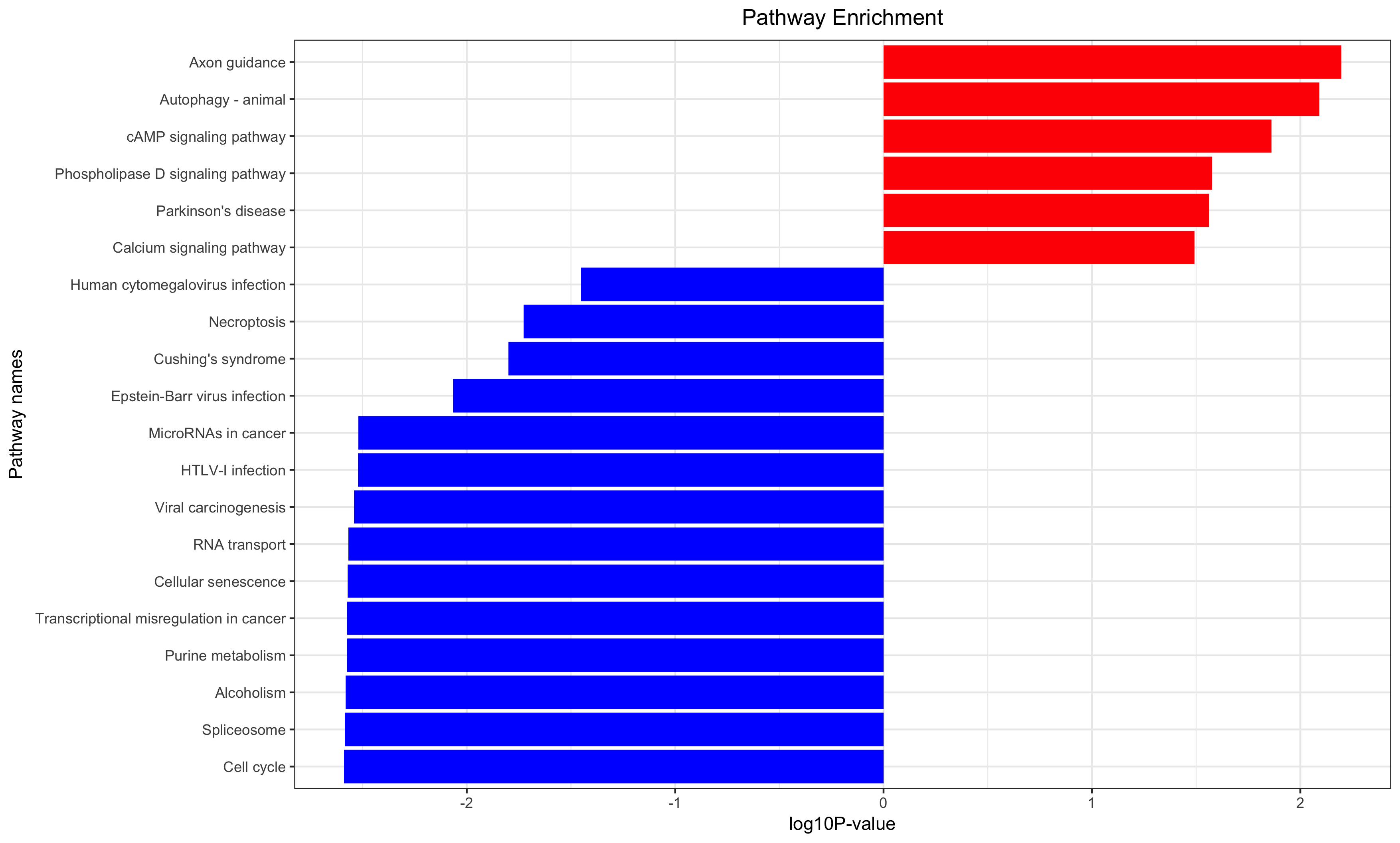
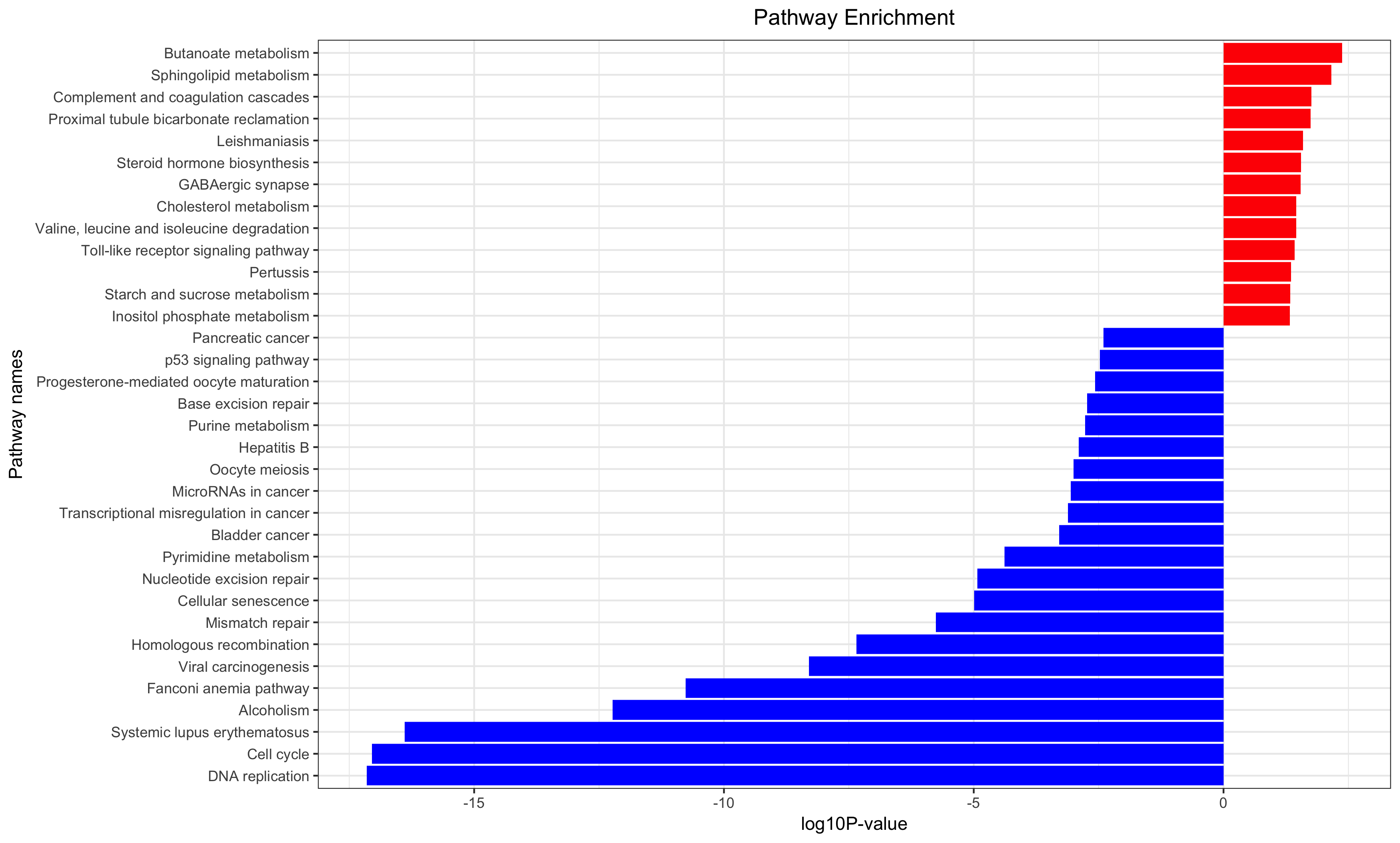
### Step5: survival analysis
生存分析是补充,只有样本量足够,而且样本的临床信息足够才能做这样的分析。
KM and cox ,需要掌握统计学原理。
### Step6: GSEA for Molecular Signatures Database (MSigDB)
算法是亮点,代码见文件夹
### Step7: GSVA for Molecular Signatures Database (MSigDB)
算法是门槛,代码见文件夹
### 更多其它例子
不一一介绍,请至少花费几十个小时学习这些代码:
### The videos tutorials :
All the videos are uploaded in YouTube: https://www.youtube.com/channel/UC67sImqK7V8tSWHMG8azIVA/videos
如果你在中国,你可能会喜欢B站: https://www.bilibili.com/read/cv719181 ,视频链接: https://www.bilibili.com/video/av26731585/
### 番外
其实不止是针对转录组表达芯片的数据分析教材,还有转录组数据处理流程,希望你可以仔细看,还有批量生存分析等各种其它统计分析方法我也会慢慢添加。
主要是根据大家的需求啦,希望大家多多反馈和提问哈!
### 最重要的是:
如果你觉得我的教程对你有帮助,请赞赏一杯咖啡哦!
如果你的赞赏超过了50元,请在扫描赞赏的同时留下你的邮箱地址,我会发送给你一个惊喜哦!

### 广告时间
关于我们
- 我的博客:生信菜鸟团
- 我们的论坛:生信技能树
- 我们的VIP社区:
- 我们的微信公众号:
- 我们的知识星球:
- 我们的腾讯课堂:
- 请善用搜索功能:
- 发邮件向我反馈 jmzeng1314@163.com